TCGA数据库挖掘-肾细胞癌相关biomiarker筛选案例解析
嫌色细胞癌属于肾细胞癌的一种,约占4-5%。利用公共数据库数据筛选此类癌症的相关biomarker进行有效的临床诊断和预后也是公共数据分析的一个方向。这里就给大家介绍一篇文献:利用WGCNA鉴定嫌色细胞癌biomarker。
数据来源
从TCGA数据库下载嫌色细胞癌样品相关数据,共获取66/25个相关样品的表达谱数据,同时得到临床性状。同时利用GEO数据库下载数据(GSE15641)后期筛选和验证分析。
数据分析
1.数据处理与差异分析
从TCGA数据库获取的表达谱数据,利用R包“DEseq2”进行差异表达分析,进而筛选差异基因。最终以adj.P.value<0.05 & |log2FC| ≥0.585,获取了2215个差异基因(1748 up-regulated / 384 down-reguated)。GSE15641数据利用GEO2R进行差异分析,基于P.value<0.05 & |log2FC|>1 筛选到1794 个差异基因(884 up-regulated / 910 down-reguated),该部分筛选结果用于biomarker的相关验证。
2.加权基因共表达网络分析
TCGA数据筛选出的2215个差异基因参与WGCNA分析,power值选定5(R2>0.85),最终获得8个有效模块(加上grey为9,见下图A),结合临床性状分析结果表明Brown模块与pathologic_stage、survival_status等相关性更明显(见下图B)。
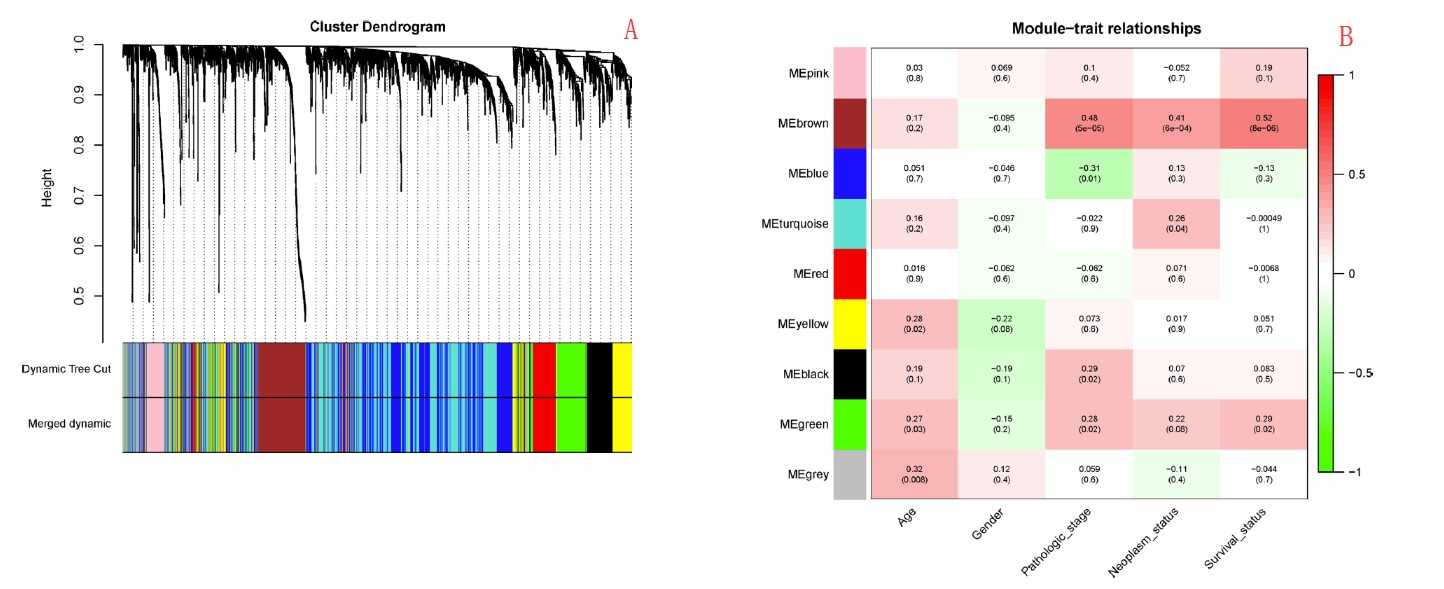
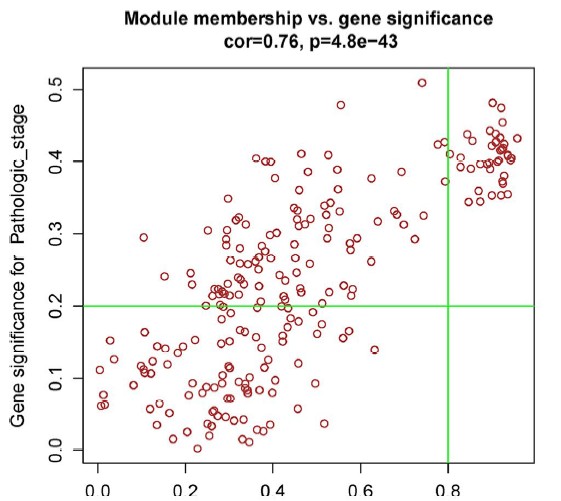
其中Brown模块内GS与MM分析结果显示,该模块内的基因与pathologic_stage显著相关(见下图),并基于MM高于0.8,GS高于0.2 筛选出了39个基因进行后期分析。
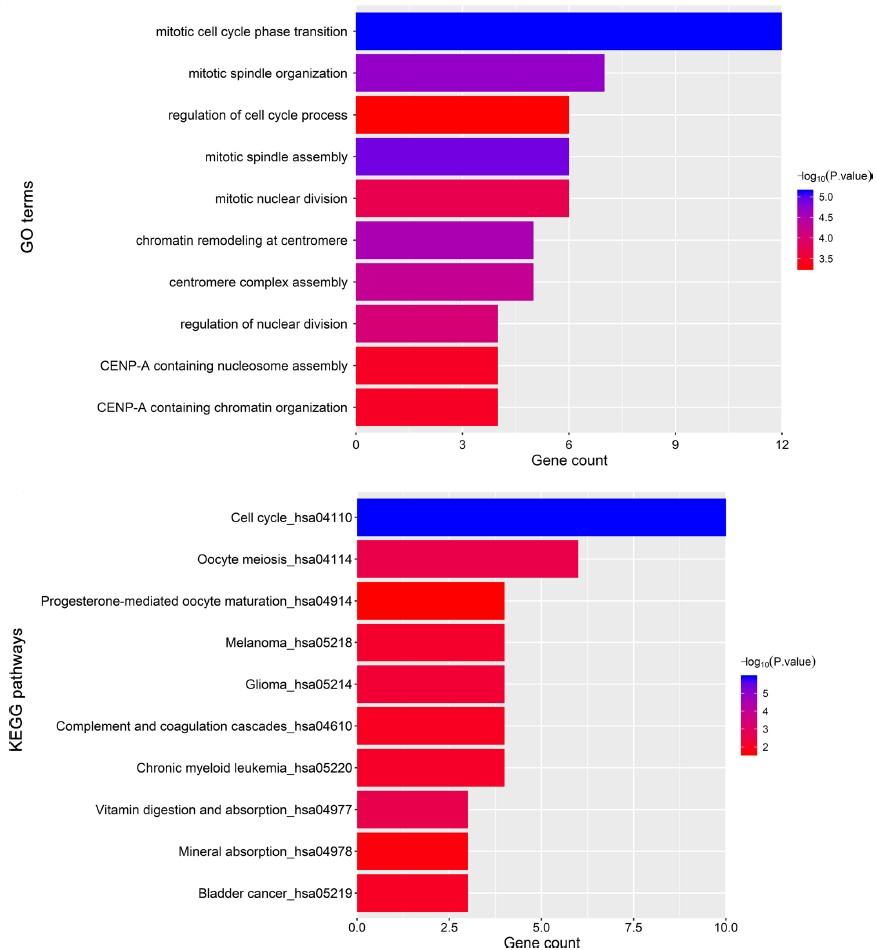
3.重要模块基因功能富集
针对Brown模块内的基因功能进行富集,从而判断这些差异基因在嫌色细胞癌中所起到的主要作用,GO富集结果显示,有丝分裂细胞周期转换、有丝分裂纺锤体组装、有丝分裂纺锤体组织,细胞周期的调节过程等相关功能显著富集;KEGG富集结果表明,细胞周期、卵母细胞减数分裂、孕酮介导的卵母细胞成熟等途径显著富集(见下图)。
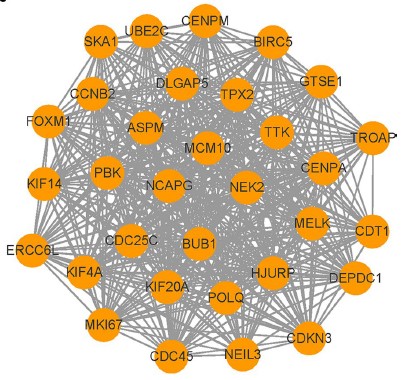
4.蛋白互作分析
为探索基因之间的蛋白互作关系,利用string数据库进行分析,最终基于brown模块所有基因获取了一个蛋白质互作网络,并借助Cytoscape软件中的MCODE软件,以k-core=2等阈值,筛选出其中关系最紧密的子网络,涉及了32个基因(下图),其中和基于模块和性状分析筛选的39个基因的重合有29个,该部分29个基因作为候选基因进一步验证。
5.筛选与验证
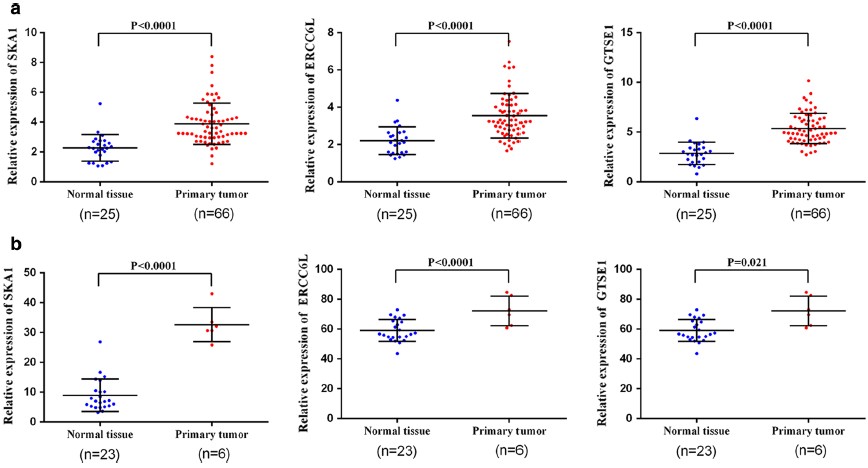
29个候选基因,结合GSE15641筛选到的差异基因,属于共有的基因有4个,其中变化趋势一致的有三个:SKA1、ERCC6L、GTSE1,此三基因在癌症样本和正常样本表达和统计分析情况见下图(A:TCGA,B: GSE15641)。
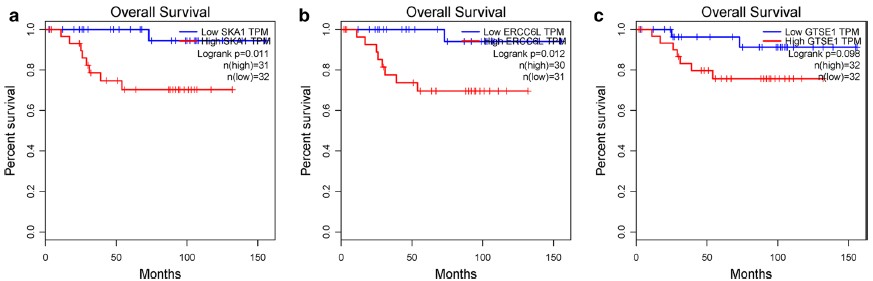
此外,进一步于GEPIA网站进行KM生存分析,最终结果显示SKA1、ERCC6L和总体生存时间更显著相关(见下图)。
结论
作者利用TCGA和GEO数据库中两项数据进行了嫌色细胞癌biomarker基因的挖掘分析,并且利用了多个在线网站工具进行了功能和互作网络方面的验证,最终结合前人的研究和自己的验证分析发现了两个基因SKA1、ERCC6L对于嫌色细胞癌的临床预后可能具备重要作用。
参考文献:Yin, X. , Wang, J. , & Zhang, J. . (2018). Identification of biomarkers of chromophobe renal cell carcinoma by weighted gene co-expression network analysis. Cancer Cell International,18(1).
相关课程:
TCGA-基因差异表达分析、 TCGA-生存分析 、 GEO芯片数据挖掘、GEO芯片数据标准化、WGCNA-加权基因共表达网络分析
更多生物信息课程:
1. 文章越来越难发?是你没发现新思路,基因家族分析发2-4分文章简单快速,学习链接:基因家族分析实操课程、基因家族文献思路解读
2. 转录组数据理解不深入?图表看不懂?点击链接学习深入解读数据结果文件,学习链接:转录组(有参)结果解读;转录组(无参)结果解读
3. 转录组数据深入挖掘技能-WGCNA,提升你的文章档次,学习链接:WGCNA-加权基因共表达网络分析
4. 转录组数据怎么挖掘?学习链接:转录组标准分析后的数据挖掘、转录组文献解读
5. 微生物16S/ITS/18S分析原理及结果解读、OTU网络图绘制、cytoscape与网络图绘制课程
6. 生物信息入门到精通必修基础课:linux系统使用、perl入门到精通、perl语言高级、R语言入门、R语言画图
7. 医学相关数据挖掘课程,不用做实验也能发文章:TCGA-差异基因分析、GEO芯片数据挖掘、GEO芯片数据标准化、GSEA富集分析课程、TCGA临床数据生存分析、TCGA-转录因子分析、TCGA-ceRNA调控网络分析
8.其他,二代测序转录组数据自主分析、NCBI数据上传、二代测序数据解读
- 发表于 2019-09-20 09:47
- 阅读 ( 5327 )
- 分类:文献解读
你可能感兴趣的文章
相关问题
- 请教一下TCGA的蛋白数据怎么理解,它是有正负值的,这个正负值代表什么意思,为什么蛋白表达会有负值?我只想给它分成高表达,低表达和表达缺失组应该怎么处理呀? 0 回答
- TCGA下载 docker报错 0 回答
- TCGA差异分析如何根据临床信息分组? 1 回答
- TCGA用R数据下载错误 1 回答
- 老师,想请教一下TCGA基因表达数据的问题,我从xena.ucsc网页上下载了基因表达数据TCGA-CESC.htseq_counts.tsv;然后发现该数据中只有Ensembl格式的基因ID ,没有SYMBOL格式的。所以接下来进行基因ID格式转换,却发现同一个SYMBOL ID对应的多个Ensembl格式的ID,想问下老师,这种情况该怎么处理?同一个SYMBOL ID所对应的多个Ensembl格式ID的基因表达数据应该留下哪一个? 1 回答
- TCGA的RNA-seq count annotation过滤,有些不知道是否需要删除 0 回答
