scanpy 绘制marker基因点图
scanpy 绘制marker基因点图
Rscript $scripts/seuratObj2anndata.r -i ../03.seurat_cluster/pbmc.qs -p harmony_seurat_clusters --assay RNA --layer data
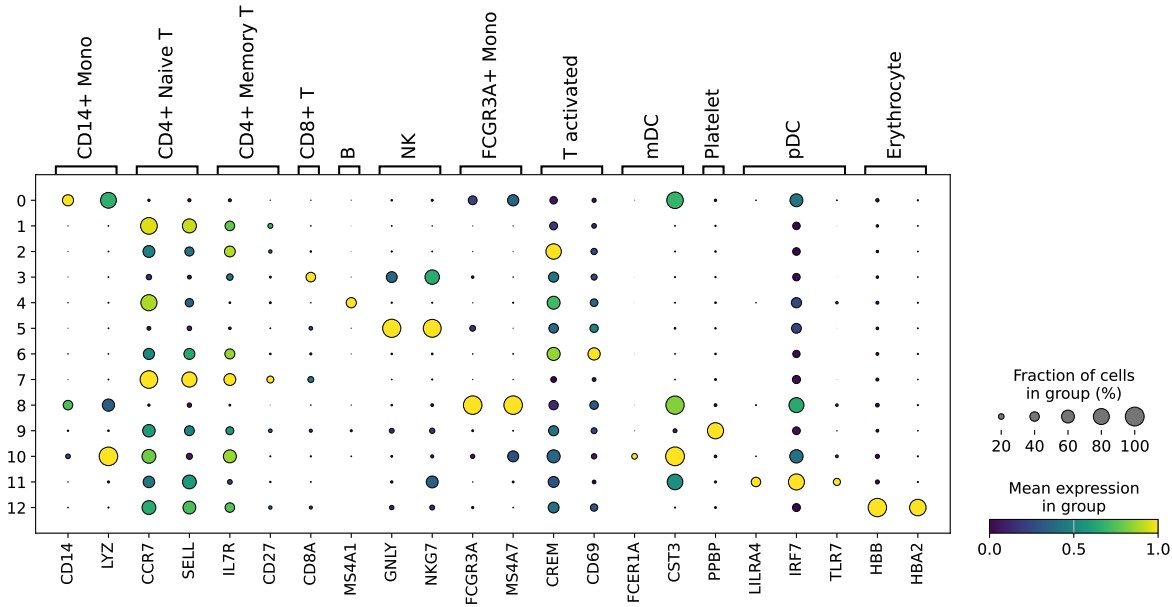
python3 $scripts/scanpy_dotplot.py -i harmony_seurat_clusters.h5ad --layer data \
--groupby seurat_clusters -p Marker.seurat_clusters -W 15 -H 6 --color_map viridis --standard_scale var \
--var_names '{
"CD14+ Mono": ["CD14", "LYZ"],
"CD4+ Naive T": ["CCR7","SELL"],
"CD4+ Memory T": [ "IL7R","CD27"],
"CD8+ T": ["CD8A"],
"B": ["MS4A1"],
"NK": ["GNLY", "NKG7"],
"FCGR3A+ Mono": ["FCGR3A", "MS4A7"],
"T activated": ["CREM", "CD69"],
"mDC": ["FCER1A", "CST3"],
"Platelet": ["PPBP"],
"pDC": ["LILRA4", "IRF7", "TLR7"],
"Erythrocyte": ["HBB", "HBA2"]
}'
- 发表于 6天前
- 阅读 ( 79 )
- 分类:转录组
你可能感兴趣的文章
- 玉米根单细胞转录组细胞类型注释代码 30 浏览
- 华大DNBC4单细胞转录组数据分析-拟南芥根愈伤组织单细胞转录组图谱 58 浏览
- 植物单细胞转录组面临的挑战 132 浏览
- 植物单细胞转录组文章 2049 浏览
- 拟南芥叶单细胞分析流程 1725 浏览
相关问题
0 条评论
请先 登录 后评论
