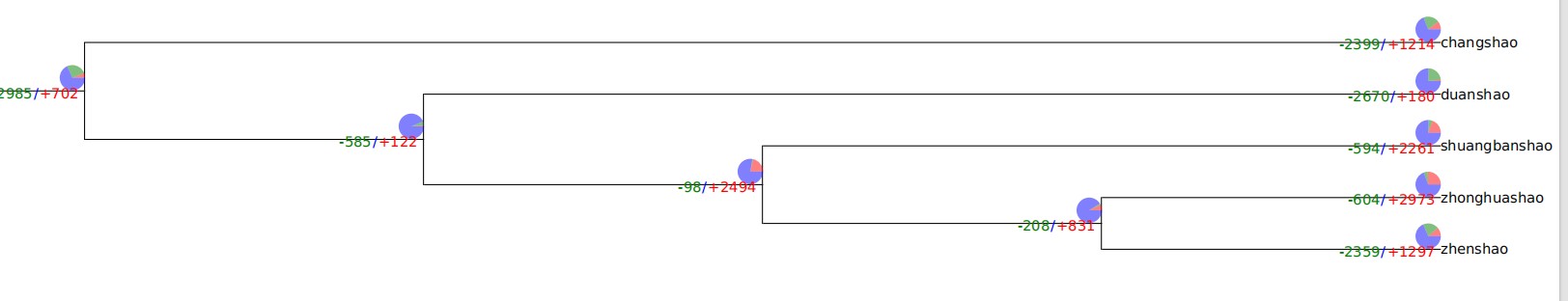
老师我想请问比较基因组的问题,我做出来了基因家族扩展收缩的问题,根据课程学习内容,我能提炼出我要研究物种的基因了,但是遇到了一个问题是,假如我想提取一类,比如头足类,该怎么把头足类的所有基因扩展收缩提出来。
- 0 关注
- 0 收藏,2160 浏览
- 浪失杂货铺 提出于 2023-11-13 22:24
相似问题
- 动植物比较基因组分析实操中基因组的版本信息 2 回答
- 使用docker镜像中的OrthoFinder.py检测单拷贝直系同源基因分析报错 2 回答
- 使用OrthoFinder时单拷贝基因很少,能说说用OrthoFinder结果里的低拷贝基因去建树吗 1 回答
- 老师请问,这种OG0000.。。代表的基因家族扩增还是收缩问题,他们的具体名称在哪里对应查找,比如OG000044代表钙粘蛋白基因家族,还是什么家族有名称吗? 1 回答
- 老师我做比较基因组的时候,准备文件阶段时用ncbi 下载的基因组跑不出来cds和蛋白质文件,麻烦老师您看一下 1 回答
- ParaAT比对结果产生空的cds_aln.fasta文件 1 回答