老师您好,感谢回答。抱歉我在问题中可能没有描述清,有些术语可能用的不够专业。
具体情况是:我现在已经得到了OTU的代表序列和OTU table,然后打算给OTU代表序列使用assign命令做物种分类和注释。
我是想用blast方法(即assign_taxonomy.py -m blast -r 参比序列数据库 -t 参比序列id)进行物种分类后,先把非目标序列从OTU表格中剔除掉,然后再做后续分析。
目前这个assign_taxonomy.py操作在执行上没有问题。但就是发现,通过blast方法比对-分类时,由于qiime默认的blast相似度阈值比较低,导致很多不是目标微生物的片段(因有不少非特异性扩增)也可以和参比序列数据库比对上,所以我无法在分类注释结果中把它们和真正的目的片段区分开。
这个我已初步试过,即通过调整blast的e value(即在assign命令后加-e命令,如-e 1e-50)后,可以大幅改善注释结果,很多非目标序列的注释结果都会变成no blast hit,不会再被assign一个分类结果。
但是现在的问题是,我发现仅靠修改e值是不够的。我后续手动在NCBI上用blastn检查了一些调整e值后可以注释上的序列,发现很多序列e值虽然比较好,但是blast score和identity什么的非常低,说明它们可能仍然不是目标序列。
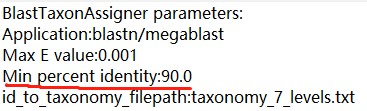
所以现在想通过继续提高其它blast的阈值来实现。但不知具体改如何操作,不知assign命令下的blast方法,除了e value外,还有没有办法可以调整其它阈值。。。?
例如,我看一些文献中,在用blast给序列分类注释时,除了会把e值设为1e-50外,还设置了如blast score > 200, identity >97%之类的,这些在qiime里该如何实现?